癌症基因组图谱(The Cancer Genome Atlas,TCGA)早已在全世界广为知晓,这项计划包含了人类全部癌症的基因组变异图谱,通过数据挖掘能够很好地了解癌症发生和发展的机制,是肿瘤研究中重要的数据库。然而,因为其数据集规模较大,复杂度较高,下载数据进行分析困难较多,很多小伙伴在下载TCGA数据时就因为诸多因素而无从下手。于是,GEPIA等基于TCGA数据库的可视化网络平台给我们带了极大的便利,能够简单快速的预测或分析绘图。今天我又为大家带来一款2020年最新的基于TCGA数据库的网络分析工具——KRAB ZNF explorer(http://mi2.mini.pw.edu.pl:8080/KRAB_ZNF/)。
这款工具是发表于今年2月的生信老牌期刊Bioinformatics,2019年最新影响因子5.61。题名为“KRAB ZNF explorer(KRAB ZNF explorer – the online tool for the exploration of the tranomic profiles of KRAB-ZNF factors in The Cancer Genome Atlas)”。作者是波兰首都华沙大学的Cylwa,Biecek等人。

背景知识
KRAB-ZNFs(Krüppel-associated box domain zinc finger proteins):是最大的锌指蛋白家族,也是最大的表观遗传抑制剂。这些蛋白在细胞信号转导、细胞生长、分化中起到重要作用。KRAB-ZNFs家族中的一些成员也参与癌症的发生发展。然而,大多数krabb - znf因子的功能仍不清楚或缺乏特征。KRAB-ZNFs参与癌症发展,因此可能支持未来探索krabi - znf作为生物标志物或抗癌靶点在患者管理机制中的功能和潜在效用的研究。
这个平台收录了381种KRAB-ZNF在30多种TCGA癌症中的功能,揭示KRAB-ZNF家族因子参与癌症的新的线索,能够进行的主要分析包括:
1)正常和肿瘤样品之间KRAB-ZNF基因的比较分析;
2)KRAB-ZNF表达与各种临床病理参数的相关性;
3)患者存活率与KRAB-ZNF基因表达之间的联系的分析和可视化;
4)分析KRAB-ZNF表达与CpG甲基化状态之间的关系;
5)分析正常和肿瘤样品中KRAB-ZNF基因的同工型表达;
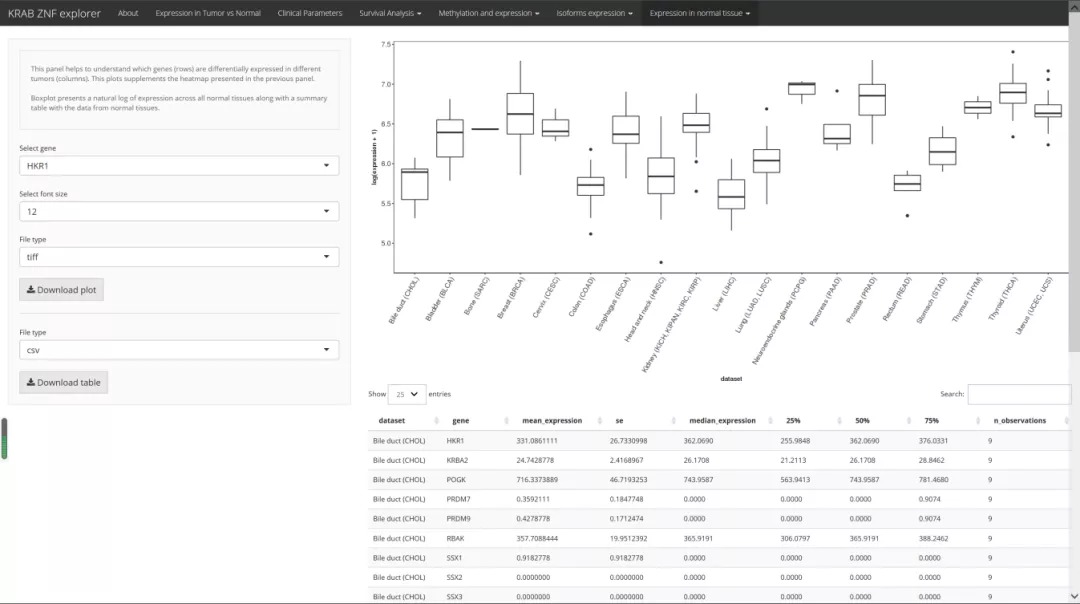
6)正常组织中KRAB-ZNF表达的比较分析
下面我们就来逐一展示这个神器的各种功能吧。
操作演示
正常组织和癌症组织KRAB-ZNF表达的比较分析
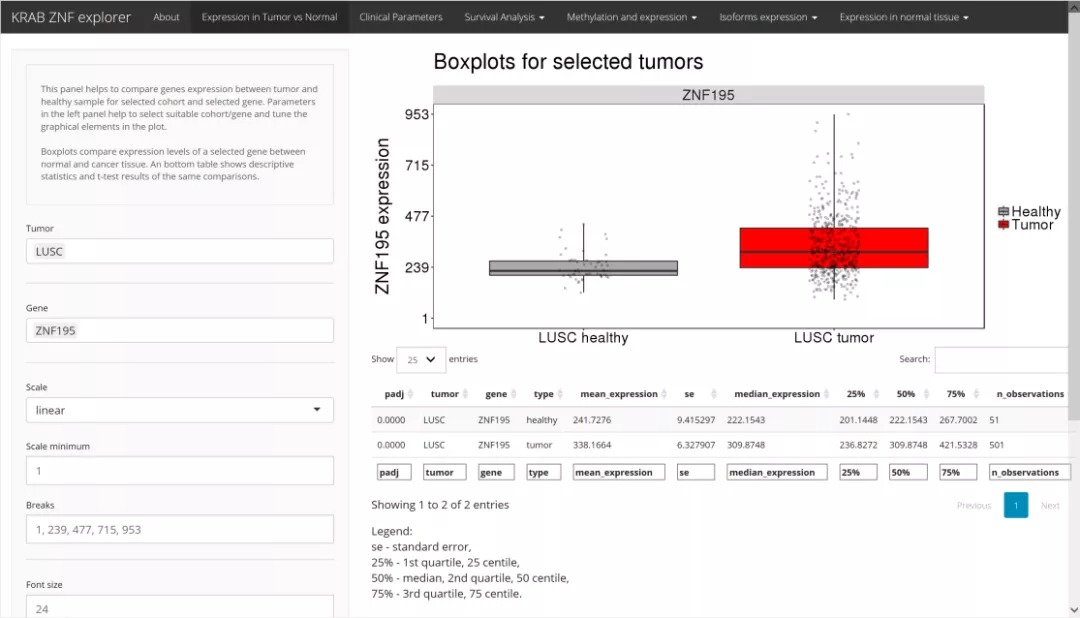
“Expression in Normal vs Tumor” 分析模块使用的是标准化的RNA-seq数据,使用错误发现率(FDR)校正的Student t检验,可以在癌症和正常组织之间进行差异表达分析。 用户可以从 数据可以可视化为箱线图。 此外,还会生成带有所需比较的t检验结果的表格,并可以下载该表格。首先我们点击“Expression in Normal vs Tumor”,接下来在页面左边,选择感兴趣的KRAB-ZNF因子和癌症类型。我们以ZNF195在LUSC中的表达为例,设定相应参数。网页自动运行,界面右方会得到结果图片和数据,下拉页面可以下载tiff, pdf, eps三种格式图片,以及csv, txt格式数据。
KRAB-ZNF表达与各种临床病理参数的相关性
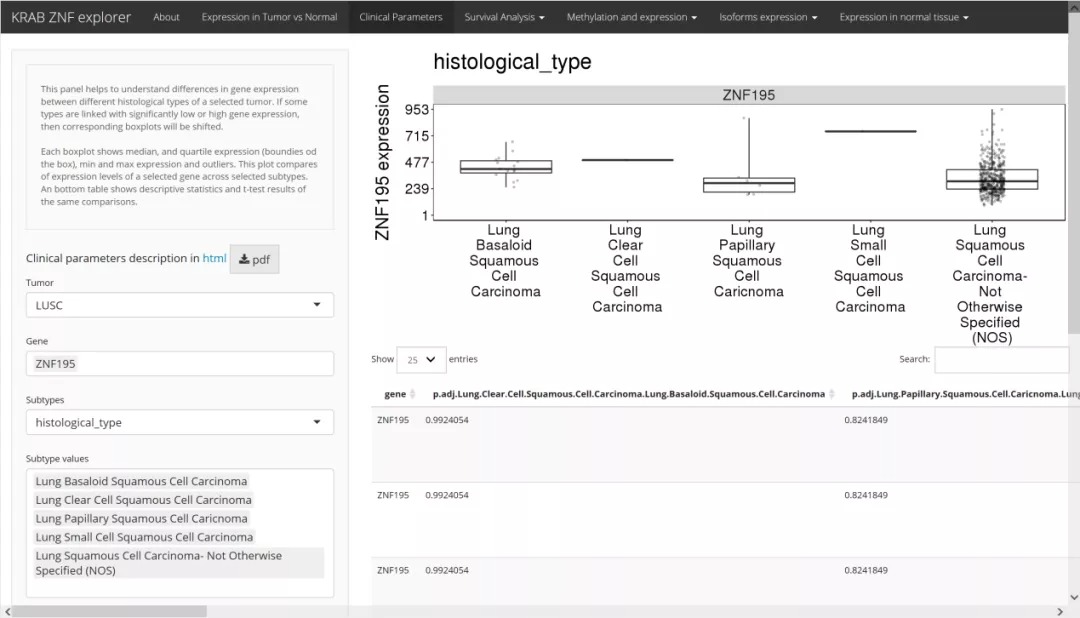
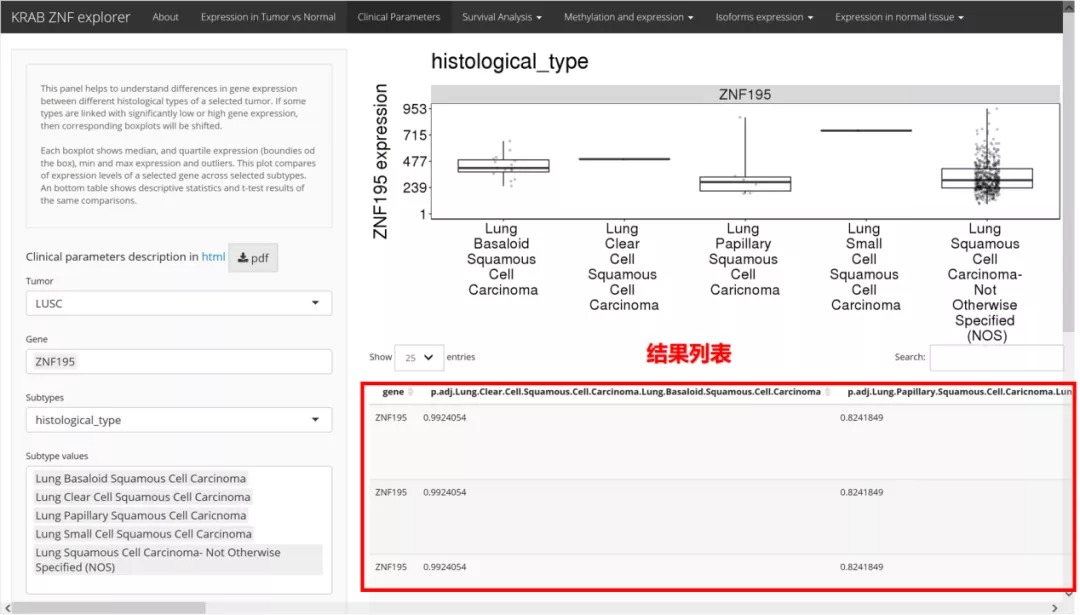
“Clinical Parameters”模块可以显示所选KRAB-ZNF因子与不同临床参数之间的相关性。同样使用带有FDR校正功能的Student t检验来评估独立亚组在临床变量和分子参数方面的差异。并通过箱式图和带有t检验结果的列表展示相应结果。该模块有助于了解所选肿瘤的不同组织学类型之间基因表达的差异。如果某些类型与显着的低基因表达或高基因表达有关,那么相应的箱形图将发生变化。每个箱线图显示中位数和四分位数表达(框的边界),最小和最大表达以及离群值。 结果箱式图比较了所选亚型中所选基因的表达水平。底部表格显示了相同比较的描述性统计数据和t检验结果。
我们仍以LUSC cohort,ZNF195基因为例,在肿瘤亚组“subtype”一栏,有“expression subtype”, “gender”, “histological type”, “smoking history”,“pathologic M” , “pathologic T”, “pathologic N” 等亚组分类可以选择。然后设置linear scale 或者log scale, 以及对scale minimum ,font size进行设定,就可以在界面右边得到可供下载的结果图片和数据。
生存分析
“Survival Analysis”模块是生存分析,提供了以下三个分析模式。

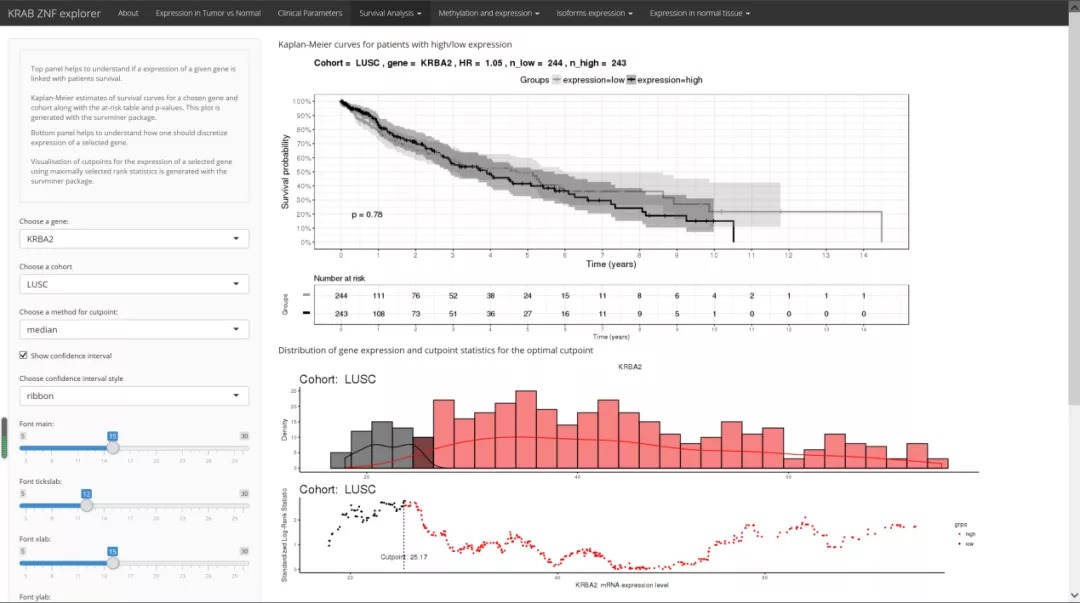
可以比较每个KRAB-ZNF在高表达和低表达组之间的个体存活率。我们可以通过表达中位值,或者使用最大选择的等级统计信息来确定分割的最佳切割点,这两种方式选择分类为高或低表达水平。并通过最大秩统计和对数秩检验的p值热图可视化切割点选择,比较各组之间的生存分布。除了绘图外,它还提供可下载的表格以及对数排名的测试结果。 使用survminer软件包进行生存分析,绘制Kaplan-Meier曲线。并可以各种格式下载并具有其他可自定义功能。我们以基因KRBA2在LUSC队列中的生存分析为例,并以系统默认参数进行设定,在界面右边出现Kaplan-Meier曲线以及基因表达的分布。可以下载png, pdf, eps, tiff四种格式。另外还可以绘制所选基因热图;生成log-rank检验表格。
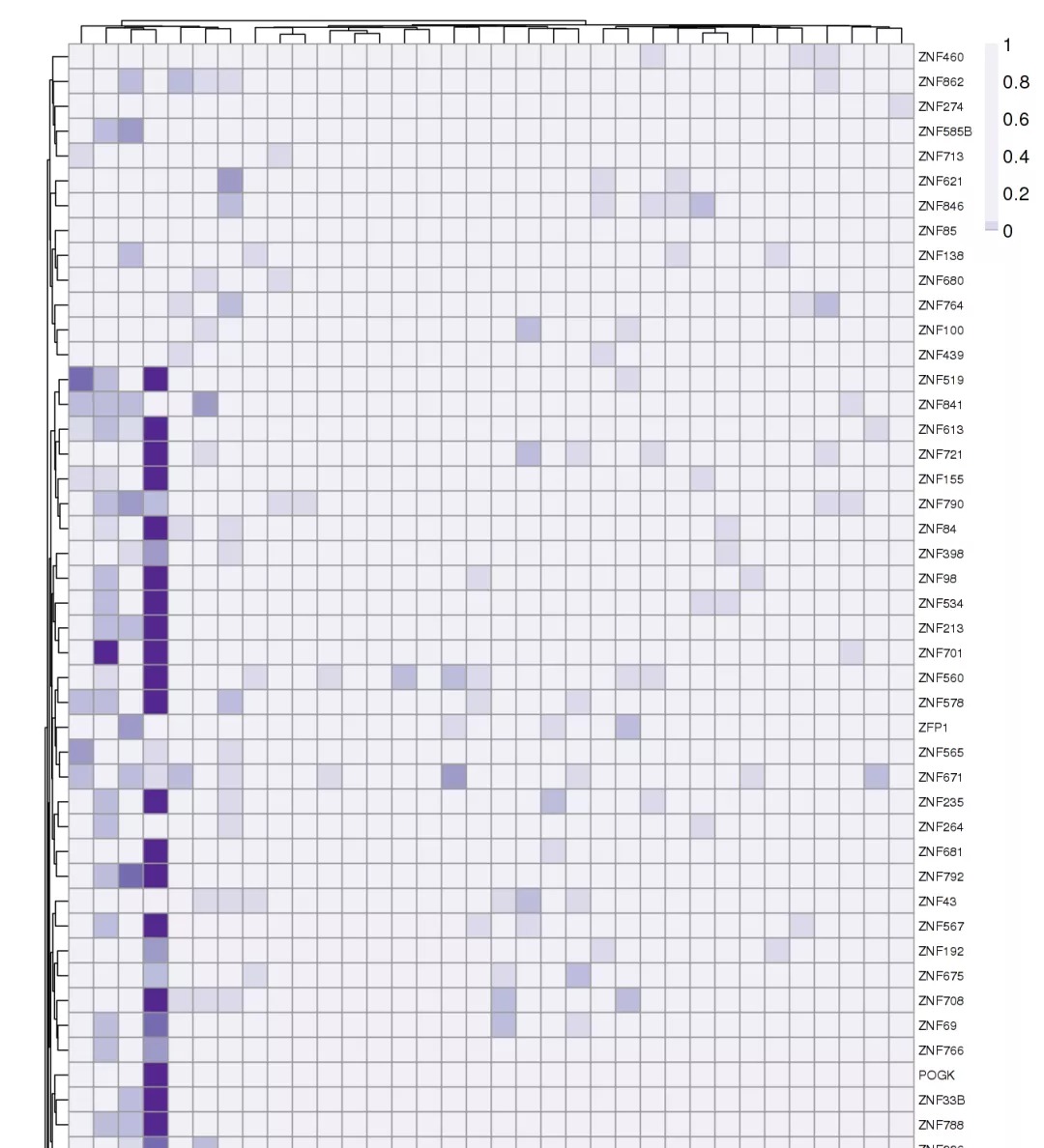
KRAB-ZNF表达与DNA甲基化的相关性
在“Methylation and Expression”模块中,我们可以分析KRAB-ZNF表达与CpG甲基化之间的相关性。分析使用了t检验以评估两组患者之间每个CpG岛的甲基化差异。 将患者以每个KRAB-ZNF和癌症队列中最高(最高10%)和最低(最低10%)表达水平分组。同样可下载结果表格。列表显示了针对每个队列进行的KRAB-ZNF因子高表达(前10%)和低表达(下10%)组之间甲基化水平差异的t-检验(p值经过FDR调整)的结果,并与基因分开。这里有可能很耗时,因为系统需要处理所有的CpG岛。
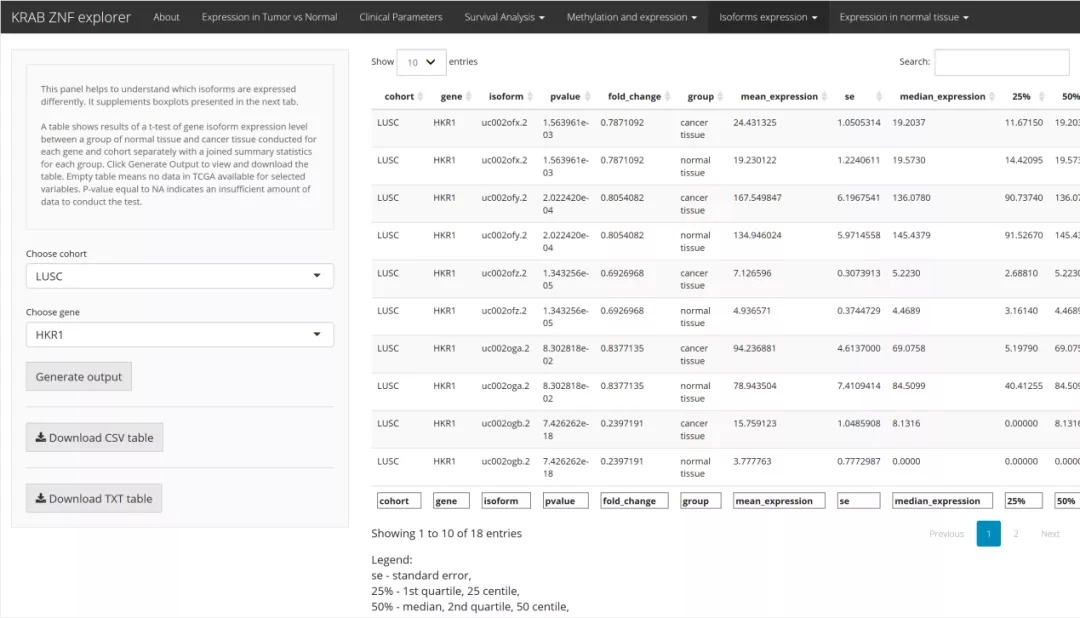
KRAB-ZNF异构体分析

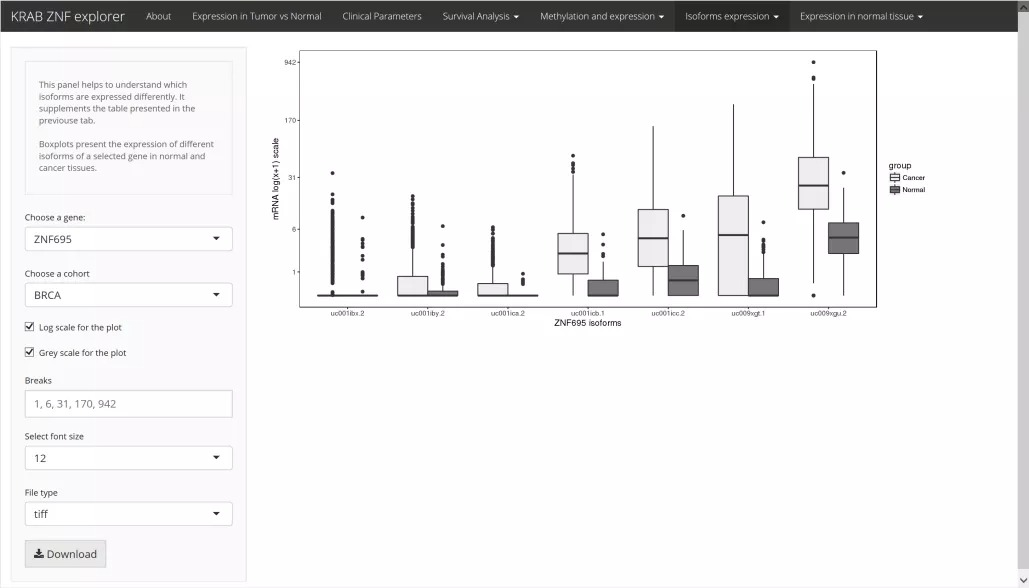
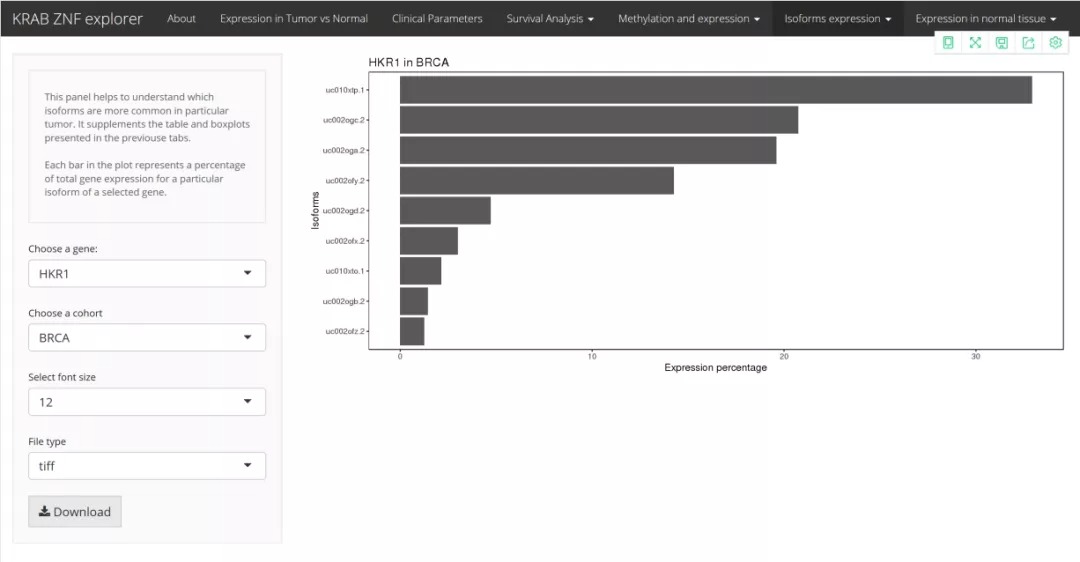
KRAB-ZNF在正常组织中的对比分析
小结
[1] Cylwa Rafał,Kiełczewski Kornel,Machnik Marta et al. KRAB ZNF explorer-the online tool for the exploration of the tranomic profiles of KRAB-ZNF factors in The Cancer Genome Atlas.[J] .Bioinformatics, 2020, 36: 980-981.
[2] Marcin Kosinski and Przemyslaw Biecek (2019). RTCGA: The Cancer Genome Atlas Data Integration. R package version 1.14.0. https://rtcga.github.io/RTCGA
[3] Marta Machnik, Rafal Cylwa, Kornel Kielczewski, Przemyslaw Biecek, Triantafillos Liloglou, Andrzej Mackiewicz, and Urszula Oleksiewicz (2019). The expression signature of cancer-associated KRAB-ZNF factors identified in TCGA pan-cancer transcriptomic data.. Mol Oncol. 2019 Apr;13(4):701-724. doi: 10.1002/1878-0261.12407.














